Amyloidum beta
|
Cave: notitiae huius paginae nec praescriptiones nec consilia medica sunt. |
| Amyloidum beta | |||||
|---|---|---|---|---|---|
| Alia nomina | Aß, Abeta | ||||
| Fontes externae | OMIM: 104760 | ||||
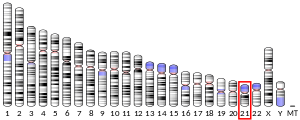
| Locus geni proteini praecursoris amyloidi (homo) | |||||
| Chromosoma | 21 (humanum) | ||||
Amyloidum beta sunt peptida 36-43 aminoacidorum, quae in morbo Alzheimeriano factores morbi principales videntur[2], ubi in aegrotorum cerebris mortuorum microscopio "plaques" (maculae) extracellulares aggregata inveniuntur.
Generata sunt amyloida beta de magis maiore proteino praecursoris amyloidi beta (APP) desectionibus enzymorum duorum ope, primo beta-secretasis 1, deinde complexus enzymatici gamma-secretasis. Investigationes histopathologicae, liquoris cerebrospinalis, et hodie Positronibus Emissis Tomographia (PET) ligandibus amyloidi beta distributionis onerisque quaesitionem etiam in vivo permittunt.
Mutatio A673T geni APP, in Islandia nota, initium morbi Alzheimeriani retardat[3]. In plerisque typis angiopathiae amyloido cerebralis (AAC) amyloidum beta repertum est.
Amyloida in genere sunt proteina unius typi aggregata in fibrillas plicantia. Amyloida idcirco non solum ex amyloidis beta constituta sunt, sed aliis morbis alia proteina in amyloidum congregentur.
Etymologia[recensere | fontem recensere]
Notio amyloidi a verbo Latino amylum derivata est. Beta ad modum plicaturae amyloidi proteini, beta-plicaturae, spectat.
Natura amyloidi beta[recensere | fontem recensere]
Amyloidum beta per gradus duos duorum enzymorum ope, beta-secretasis 1 enim et gamma-secretasis, ex proteino praecursore amyloidi dissecatus est.
Proteinum praecursor amyloidi[recensere | fontem recensere]
Proteinum praecursor amyloidi (PPA), cuius genum apud homines in chromosomate 21 invenitur, est proteinum transmembranaceum et eo opus generationis amyloidi beta est[4]. Extra cellulam longior N-terminus proteini, in cytoplasmate brevior C-terminus locati sunt. Inter eos singulare filamentum aminoacidorum trans membranam currit. Nonnullae isoformae variae longitudinis ab 695 (saepissime) ad 770 aminoacidorum descriptae sunt.
Secretases: Alpha, beta, gamma[recensere | fontem recensere]
Fortuna quidem proteini praecursoris amyloidi (PPA) vel damnum per trium actionem generum ssecretasum enzymorum constitutum iri videtur: alpha, beta, gamma secretases.
- Alpha-secretasis secat PPA extra cellulam cum effectu formationis partium solubilium sectarum
- Beta-secretasis 1 - idem, sed effectus partes non solubiles sectae oriuntur, cum momentis generationis macularum morbosarum in morbo Alzheimeriano
- Gamma-secretasis est enzymum membranae cellularis integrale, enzymum transmembranaceum PPA intra membranam cellularem secans
Amyloidum, beta-plicatura, et amyloidum beta[recensere | fontem recensere]
Generaliter dictum, amyloidum est agglomeratio proteinorum filamenta, plus vel minus longiora, formans. Nonnulli proteinorum organismi istud statum amyloideum accipere possunt, quando se in cadenas plus quam viginti quinque proteinorum mutant, quo structura beta-plicaturae formatur[5]. Prima descriptio beta-plicaturae proteinorum structura anno 1935 divulgata est[6]. Formatio amyloidorum non raro cum initio mutationum pathologicarum coniuncta videtur. Atque formatio neurofilamentorum ex amyloido beta mutationes communiter, amyloidum formans, cum degeneratione nervorum, quae substratum pathologicum Morbi Alzheimeriani est.
Variantes amyloidi beta[recensere | fontem recensere]
Longitudo aminoacidorum amyloidi beta ab triginta sex ad quadraginta tres eminet. Hac variabilitate variantes Morbi Alzheimeriani elucere postulatum est.
Pathophysiologia[recensere | fontem recensere]
In quibusque morbis neurodegenerativis, ut morbo Alzheimeriano, insignes multitudines amyloidorum beta in fibrillas elongatas intra cerebrum sub microscopio inveniri possunt. Aggregata Aß oligomera primo praefibrillares, deinde fibrillares coalescunt[7]. Cursus ab amyloido beta ad fibrillas sub microscopio visibiles plures gradus continent. Variae hypotheses initii enim decursus pathologici disputantur. Assumunt alii pathologicam plicaturam initium esse, prout alii relationem inter generationem et destructionem amyloidorum beta ad generationem proteinorum mutatam esse credunt.
Hodie in scientia praeterea dysaequilibrium inter Aß generationem et decessum putatur, Aß dyshomeostasis vocatur[8].
At systema immunitatis innatum aliquatenus mutationibus geneticis in cursum degenerativum implicari videtur[9].
Amyloidum beta et morbus Alzheimerianus[recensere | fontem recensere]
In morbo Alzheimeriano, post mortem, sub microscopio aggregatio multitudinum ß-amyloidi inveniri potest. Initio morbi amyloidum beta excitationes neuronorum provocet suppressione reabsorptionis neurotransmissoris glutamati causa[10].
Dignoscere et investigatio[recensere | fontem recensere]
Contextu cum morbis neurodegenerativis, specialiter morbo Alzheimerianus, quantitates et qualitates dignoscere et investigare res medicam scientificam sunt. In liquore cerebrospinali valor amyloidi beta supra normalem morbi suspicionem excitare potest. Hodie scientificae investigationes histologicae microscopio atque Positronibus Emissis Tomographia (PET) momentum crescens habent.
Liquor cerebrospinalis[recensere | fontem recensere]
Possunt investigari amyloidi beta diversarum longitudinum, per exemplum 40 aminoacidorum (Aß40), quadraginta duo (Aß42), et quadraginta tres (Aß43).
Positronibus Emissis Tomographia (PET)[recensere | fontem recensere]
Per liganda dicta quantitas amyloidi beta in vivo aestimari potest, igitur quaesitionem morborum neurodegenerativos iam in statu suspecto peragere licet[11]. Liganda amyloidi beta sunt 11C-PIB, 18F-florbetapir[12], 18F-florbetabenum[13], 18F-flutemetamolum[14].
Notae[recensere | fontem recensere]
- ↑ Vivekanandan S., Brender J. R., Lee S. Y., Ramamoorthy A. (2011). "A partially folded structure of amyloid-beta(1-40) in an aqueous environment.". Biochemical and biophysical research communications 411 (2): 312-6
- ↑ Walsh D. M., Teplow D. B. (2012). "Alzheimer's disease and the amyloid β-protein". Progress in molecular biology and translational science 107: 101-24.
- ↑ Jonsson T., Atwal J. K., Steinberg S., Snaedal J., Jonsson P. V., Bjornsson S., Stefansson H., Sulem P., Gudbjartsson D., Maloney J., Hoyte K., Gustafson A., Liu Y., Lu Y., Bhangale T., Graham R. R., Huttenlocher J., Bjornsdottir G., Andreassen O. A., Jönsson E. G., Palotie A., Behrens T. W., Magnusson O. T., Kong A., Thorsteinsdottir U., Watts R. J., Stefansson K. (2012). "A mutation in APP protects against Alzheimer's disease and age-related cognitive decline". Nature 488 (7409): 96-9
- ↑ Chen G. F., Xu T. H., Yan Y., Zhou Y. R., Jiang Y., Melcher K., Xu H. E. (2017). "Amyloid beta: structure, biology and structure-based therapeutic development". Acta pharmacologica Sinica 38 (9): 1205-35
- ↑ Eisenberg D., Jucker M. (2012). "The amyloid state of proteins in human diseases". Cell 148 (6): 1188–203
- ↑ Astbury W. T., Dickinson S., Bailey K. (1935). "The X-ray interpretation of denaturation and the structure of the seed globulins". Biochemical Journal 29: 2351–2360
- ↑ Breydo L., Kurouski D., Rasool S., Milton S., Wu J. W., Uversky V. N., Lednev I. K., Glabe C. G. (2016). "Structural differences between amyloid beta oligomers". Biochemical and biophysical research communications 477 (4): 700-5
- ↑ Selkoe D. J., Hardy J. (2016). "The amyloid hypothesis of Alzheimer's disease at 25 years". EMBO molecular medicine 8 (6): 595-608
- ↑ Jones L., Holmans P. A., Hamshere M. L., Harold D., Moskvina V., Ivanov D., Pocklington A., Abraham R., et al. (2010). "Genetic evidence implicates the immune system and cholesterol metabolism in the aetiology of Alzheimer's disease". PloS one 5 (11): e13950
- ↑ Zott B., Simon M. M., Hong W., Unger F., Chen-Engerer H. J., Frosch M. P., Sakmann B., Walsh D. M., Konnerth A. (Aug 2019). "A vicious cycle of β amyloid-dependent neuronal hyperactivation". Science 365 (6453): 559-65
- ↑ Chételat G., La Joie R., Villain N., Perrotin A., de La Sayette V., Eustache F., Vandenberghe R. (2013). "Amyloid imaging in cognitively normal individuals, at-risk populations and preclinical Alzheimer's disease". Neuroimage Clinical 2: 356-65
- ↑ Asghar M., Hinz R., Herholz K., Carter S. F. (2019). "Dual-phase [18Fflorbetapir in frontotemporal dementia"]. European journal of nuclear medicine and molecular imaging 46 (2): 304-11
- ↑ Alongi P., Sardina D. S., Coppola R., Scalisi S., Puglisi V., Arnone A., Raimondo G. D., Munerati E., Alaimo V., et al. (2019). "18F-Florbetaben PET/CT to Assess Alzheimer's Disease: A new Analysis Method for Regional Amyloid Quantification". Journal of neuroimaging: 10.1111/jon.12601
- ↑ Miki T., Shimada H3., Kim J. S., Yamamoto Y., Sugino M., Kowa H., Heurling K., Zanette M., Sherwin P. F., Senda M. (2017). "Brain uptake and safety of Flutemetamol F 18 injection in Japanese subjects with probable Alzheimer's disease, subjects with amnestic mild cognitive impairment and healthy volunteers". Annals of nuclear medicine 31 (3): 260-72

![Peptidum amyloidum beta[1]](http://upload.wikimedia.org/wikipedia/commons/thumb/3/36/Amyloid-beta.png/200px-Amyloid-beta.png)